Counterfactual Understanding via Retrieval-aware Multimodal Modeling for Time-to-Event Survival Prediction
作者: Ha-Anh Hoang Nguyen, Tri-Duc Phan Le, Duc-Hoang Pham, Huy-Son Nguyen, Cam-Van Thi Nguyen, Duc-Trong Le, Hoang-Quynh Le
分类: cs.LG, cs.IR
发布日期: 2026-02-23
🔗 代码/项目: GITHUB
💡 一句话要点
提出CURE框架以解决时间事件反事实生存预测问题
🎯 匹配领域: 支柱九:具身大模型 (Embodied Foundation Models)
关键词: 反事实生存预测 多模态建模 潜在亚组检索 个体化医疗 生存分析 混合专家架构 临床数据整合
📋 核心要点
- 现有的生存预测方法在处理异质性和截尾数据时存在局限性,难以优化个体化生存结果。
- CURE框架通过多模态嵌入和潜在亚组检索,整合多种信息源以提升反事实生存建模能力。
- 在METABRIC和TCGA-LUAD数据集上的实验结果显示,CURE模型在生存分析中显著优于传统基线方法。
📝 摘要(中文)
本论文针对时间事件反事实生存预测问题,旨在优化个体化生存结果,尤其在异质性和截尾数据的情况下。我们提出了CURE框架,通过全面的多模态嵌入和潜在亚组检索,推动反事实生存建模。CURE整合了临床、辅助临床、人口统计和多组学信息,并通过交叉注意力机制进行对齐和融合。复杂的多组学信号可以通过专家混合架构自适应地进行精炼,强调最具信息量的组学成分。基于此表示,CURE隐式地检索患者特定的潜在亚组,捕捉基线生存动态和治疗依赖的变化。实验结果表明,CURE模型在METABRIC和TCGA-LUAD数据集上在生存分析中始终优于强基线,显示了CURE在多模态理解中的潜力,并为未来的治疗推荐模型奠定基础。
🔬 方法详解
问题定义:本论文旨在解决时间事件反事实生存预测中的个体化生存结果优化问题。现有方法在处理异质性和截尾数据时存在不足,无法有效捕捉患者的生存动态和治疗效果的变化。
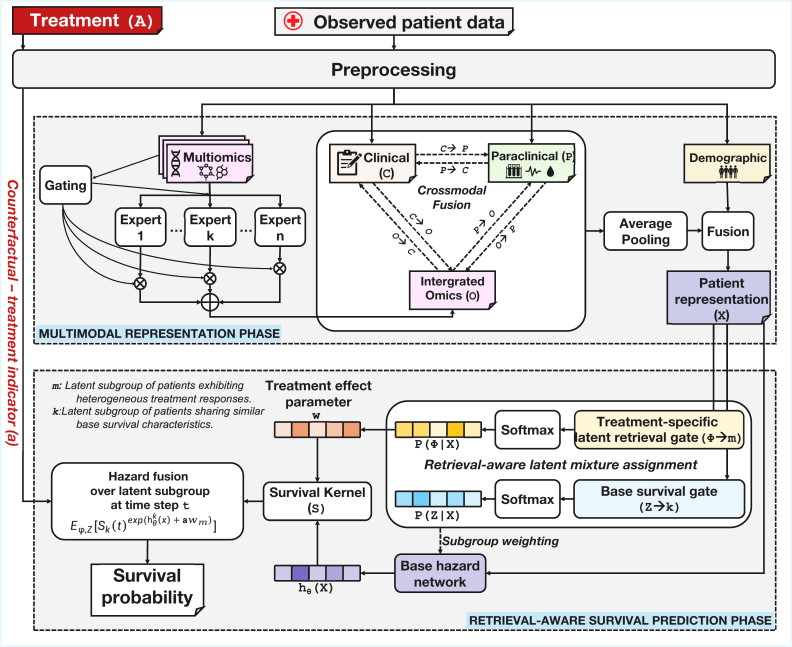
核心思路:CURE框架的核心思路是通过综合多模态信息和潜在亚组检索来增强反事实生存建模能力。通过交叉注意力机制对不同信息源进行对齐和融合,CURE能够更好地捕捉复杂的生存动态。
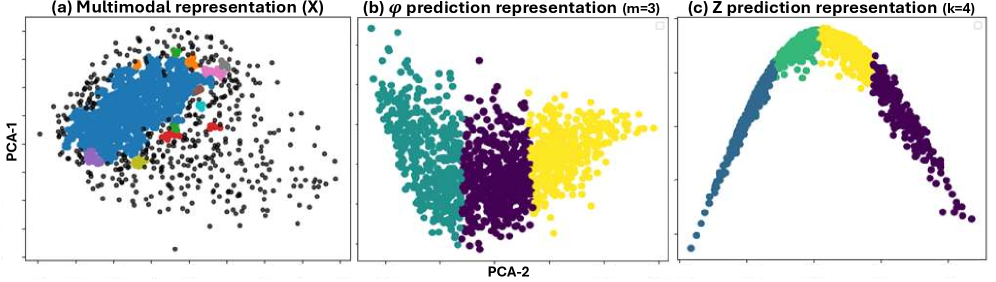
技术框架:CURE的整体架构包括多个主要模块:首先,整合临床、辅助临床、人口统计和多组学信息;其次,通过交叉注意力机制进行信息对齐和融合;最后,利用专家混合架构自适应精炼多组学信号,并隐式检索患者特定的潜在亚组。
关键创新:CURE的最重要创新在于其综合多模态信息的能力和潜在亚组检索机制,这与现有方法的单一信息源处理方式形成了本质区别。
关键设计:CURE采用了混合专家架构来强调最具信息量的组学成分,并设计了适应性损失函数以优化生存预测性能。
🖼️ 关键图片
📊 实验亮点
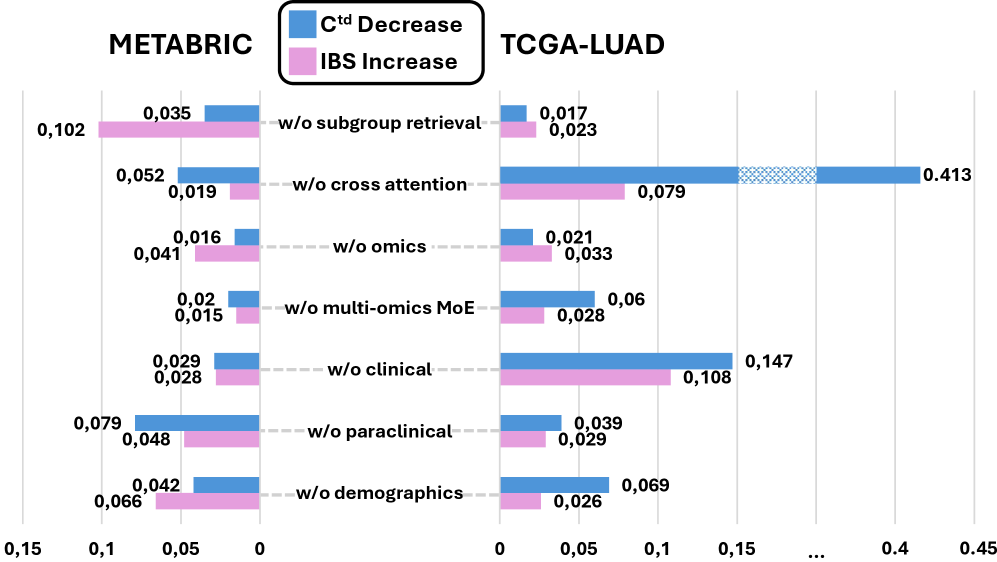
实验结果表明,CURE模型在METABRIC和TCGA-LUAD数据集上的表现优于多个强基线方法,具体在生存分析中,CURE的时间依赖一致性指数($C^{td}$)和综合Brier评分(IBS)均显示出显著提升,验证了其有效性和可靠性。
🎯 应用场景
该研究在个体化医疗、临床决策支持和生存分析等领域具有广泛的潜在应用价值。通过优化生存预测,CURE框架可以为患者提供更精准的治疗建议,提升治疗效果,并为未来的个性化治疗推荐模型奠定基础。
📄 摘要(原文)
This paper tackles the problem of time-to-event counterfactual survival prediction, aiming to optimize individualized survival outcomes in the presence of heterogeneity and censored data. We propose CURE, a framework that advances counterfactual survival modeling via comprehensive multimodal embedding and latent subgroup retrieval. CURE integrates clinical, paraclinical, demographic, and multi-omics information, which are aligned and fused through cross-attention mechanisms. Complex multi-omics signals can be adaptively refined using a mixture-of-experts architecture, emphasizing the most informative omics components. Building upon this representation, CURE implicitly retrieves patient-specific latent subgroups that capture both baseline survival dynamics and treatment-dependent variations. Experimental results on METABRIC and TCGA-LUAD datasets demonstrate that proposed CURE model consistently outperforms strong baselines in survival analysis, evaluated using the Time-dependent Concordance Index ($C^{td}$) and Integrated Brier Score (IBS). These findings highlight the potential of CURE to enhance multimodal understanding and serve as a foundation for future treatment recommendation models. All code and related resources are publicly available to facilitate the reproducibility https://github.com/L2R-UET/CURE.