Large Language Model is Secretly a Protein Sequence Optimizer
作者: Yinkai Wang, Jiaxing He, Yuanqi Du, Xiaohui Chen, Jianan Canal Li, Li-Ping Liu, Xiaolin Xu, Soha Hassoun
分类: cs.LG, cs.AI, q-bio.QM
发布日期: 2025-01-16 (更新: 2025-01-17)
备注: Preprint
💡 一句话要点
利用大语言模型进行蛋白质序列优化,实现定向进化
🎯 匹配领域: 支柱九:具身大模型 (Embodied Foundation Models)
关键词: 蛋白质工程 序列优化 大语言模型 定向进化 适应度景观
📋 核心要点
- 蛋白质序列工程旨在寻找具有更高适应度的蛋白质序列,传统方法依赖于耗时耗力的定向进化实验。
- 本文提出利用大语言模型(LLM)作为蛋白质序列优化器,通过定向进化方法进行蛋白质工程。
- 实验表明,该方法在合成和实验适应度景观上均表现出良好的优化性能,证明了LLM在蛋白质工程中的潜力。
📝 摘要(中文)
本文研究蛋白质序列工程问题,旨在从给定的野生型序列出发,找到具有更高适应度水平的蛋白质序列。定向进化是该领域的主流范式,它通过迭代过程生成变体并通过实验反馈进行选择。本文证明,尽管大语言模型(LLM)是在海量文本上训练的,但它们实际上是蛋白质序列优化器。通过定向进化方法,LLM可以通过帕累托和实验预算约束优化来执行蛋白质工程,并在合成和实验适应度景观上都取得了成功。
🔬 方法详解
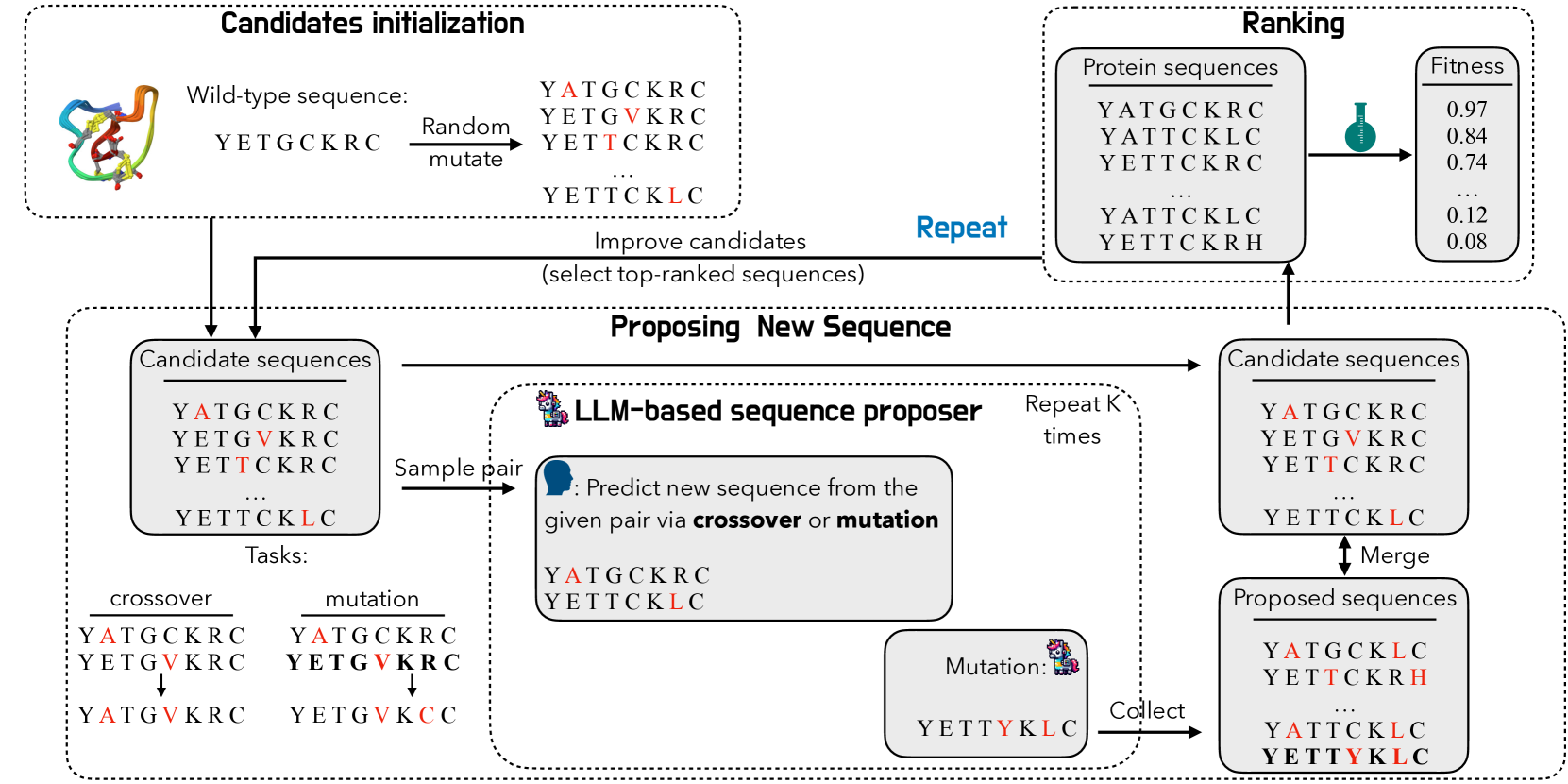
问题定义:蛋白质序列工程旨在从给定的野生型序列出发,寻找具有更高适应度水平的蛋白质序列。传统的定向进化方法需要进行大量的实验迭代,成本高昂且效率低下。如何利用计算方法加速蛋白质序列优化,降低实验成本,是本文要解决的核心问题。
核心思路:本文的核心思路是将大语言模型(LLM)视为蛋白质序列优化器。LLM在海量文本数据上训练,学习到了丰富的语言模式和知识。作者认为,这些知识可以迁移到蛋白质序列优化任务中,指导序列变异,从而提高适应度。
技术框架:该方法采用定向进化框架,主要包含以下几个阶段:1) 初始化:从给定的野生型序列开始。2) 变异:利用LLM生成蛋白质序列变体。3) 评估:通过实验或计算方法评估变体的适应度。4) 选择:根据适应度选择优秀的变体,作为下一轮迭代的起始序列。5) 迭代:重复上述步骤,直到达到预定的迭代次数或实验预算。
关键创新:本文最重要的创新点在于将LLM应用于蛋白质序列优化。与传统的基于规则或统计模型的变异方法相比,LLM能够生成更具多样性和创新性的序列变体,从而加速优化过程。此外,本文还提出了帕累托和实验预算约束优化方法,进一步提高了优化效率。
关键设计:在变异阶段,作者使用了不同的提示策略(prompting strategies)来引导LLM生成具有特定性质的序列变体。例如,可以使用“增加稳定性”或“提高活性”等提示语,引导LLM生成具有相应功能的序列。此外,作者还探索了不同的LLM架构和训练方法,以提高LLM在蛋白质序列优化任务中的性能。具体参数设置和损失函数等细节在论文中进行了详细描述(未知)。
🖼️ 关键图片
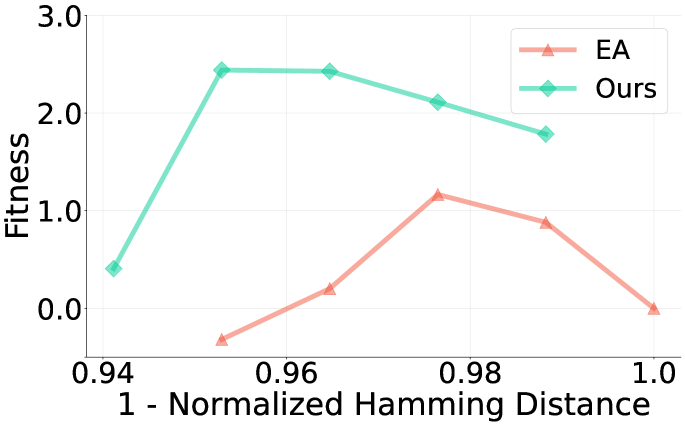
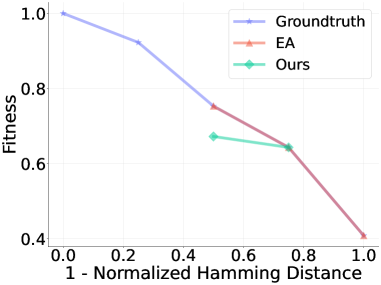
📊 实验亮点
本文通过合成和实验适应度景观验证了该方法的有效性。实验结果表明,与传统的定向进化方法相比,该方法能够在更少的迭代次数和更低的实验预算下,找到具有更高适应度的蛋白质序列。具体的性能提升幅度在论文中进行了详细的量化分析(未知)。
🎯 应用场景
该研究成果具有广泛的应用前景,可用于蛋白质药物设计、酶工程、生物材料开发等领域。通过利用LLM加速蛋白质序列优化,可以显著降低研发成本,缩短研发周期,并发现具有更优性能的蛋白质序列,从而推动相关领域的发展。
📄 摘要(原文)
We consider the protein sequence engineering problem, which aims to find protein sequences with high fitness levels, starting from a given wild-type sequence. Directed evolution has been a dominating paradigm in this field which has an iterative process to generate variants and select via experimental feedback. We demonstrate large language models (LLMs), despite being trained on massive texts, are secretly protein sequence optimizers. With a directed evolutionary method, LLM can perform protein engineering through Pareto and experiment-budget constrained optimization, demonstrating success on both synthetic and experimental fitness landscapes.