Higher-Order Message Passing for Glycan Representation Learning
作者: Roman Joeres, Daniel Bojar
分类: cs.LG, q-bio.BM
发布日期: 2024-09-20 (更新: 2025-02-11)
备注: Accepted to MLSB Workshop at NeurIPS 2024
💡 一句话要点
提出基于高阶消息传递的组合复形网络,用于糖链表示学习,刷新GlycanML benchmark性能。
🎯 匹配领域: 支柱二:RL算法与架构 (RL & Architecture)
关键词: 糖链表示学习 图神经网络 高阶消息传递 组合复形 GlycanML 计算糖科学
📋 核心要点
- 现有糖链预测模型不足,难以应对糖链的多样性和复杂性,无法充分揭示其生物学功能。
- 利用组合复形和高阶消息传递,从糖链结构中提取特征,学习其在潜在空间的有效表示。
- 在改进的GlycanML benchmark上评估,模型性能达到新的state-of-the-art水平,推动计算糖科学发展。
📝 摘要(中文)
糖链是最复杂的生物序列,由单糖形成扩展的非线性序列。作为翻译后修饰,它们调节蛋白质的结构、功能和相互作用。由于其多样性和复杂性,目前对糖链性质和功能的预测模型仍然不足。图神经网络(GNN)是为处理和分析图结构数据而设计的深度学习模型。这些架构利用图中的连接性和关系信息来学习节点、边和整个图的有效表示。通过迭代地聚合来自相邻节点的信息,GNN能够捕获图数据中复杂的模式,使其特别适合于跨领域的链接预测或图分类等任务。本研究提出了一种基于组合复形和高阶消息传递的新模型架构,用于从糖链结构中提取特征到潜在空间表示。该架构在改进的GlycanML benchmark套件上进行了评估,建立了新的state-of-the-art性能。我们设想这些改进将促进计算糖科学的进一步发展,并揭示糖链在生物学中的作用。
🔬 方法详解
问题定义:论文旨在解决糖链表示学习的问题。现有方法难以有效捕捉糖链复杂的非线性结构和单糖之间的关系,导致预测糖链性质和功能的模型性能不足。传统的GNN方法可能无法充分利用糖链中存在的高阶关系,限制了其表示能力。
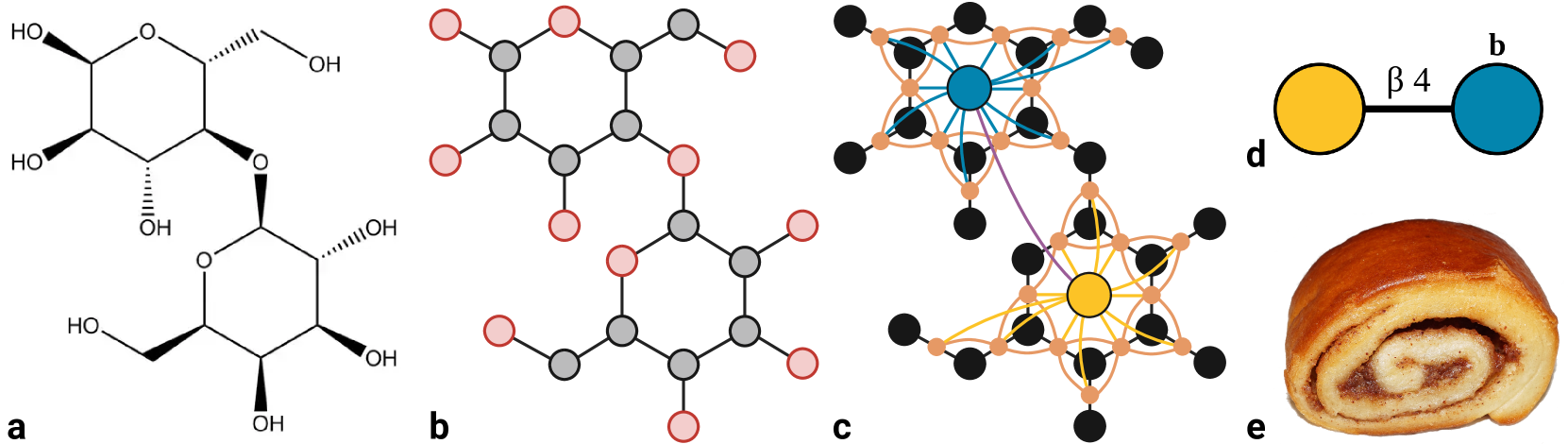
核心思路:论文的核心思路是利用组合复形和高阶消息传递来更好地表示糖链结构。组合复形能够捕捉节点之间的高阶关系,而高阶消息传递允许信息在更远的节点之间传播,从而更全面地理解糖链的结构特征。通过这种方式,模型能够学习到更具表达力的糖链表示。
技术框架:该模型架构基于图神经网络,但引入了组合复形的概念。整体流程包括:1) 将糖链结构转化为图结构;2) 构建基于组合复形的图表示;3) 使用高阶消息传递机制在图上传播信息,学习节点和图的表示;4) 利用学习到的表示进行下游任务的预测,如糖链性质预测或功能预测。
关键创新:最重要的技术创新点在于使用组合复形和高阶消息传递来增强GNN的表示能力。与传统的GNN相比,该方法能够捕捉糖链中更复杂的关系,从而学习到更有效的表示。这种方法能够更好地利用糖链的结构信息,提高预测性能。
关键设计:论文中可能涉及的关键设计包括:1) 如何构建组合复形,例如选择哪些高阶结构(如三角形、四面体等);2) 高阶消息传递的具体实现方式,例如如何定义消息传递函数和聚合函数;3) 损失函数的选择,例如使用交叉熵损失或均方误差损失,以及是否引入正则化项;4) 网络结构的参数设置,例如隐藏层的大小、消息传递的轮数等。(具体细节未知,需参考论文正文)
🖼️ 关键图片

📊 实验亮点
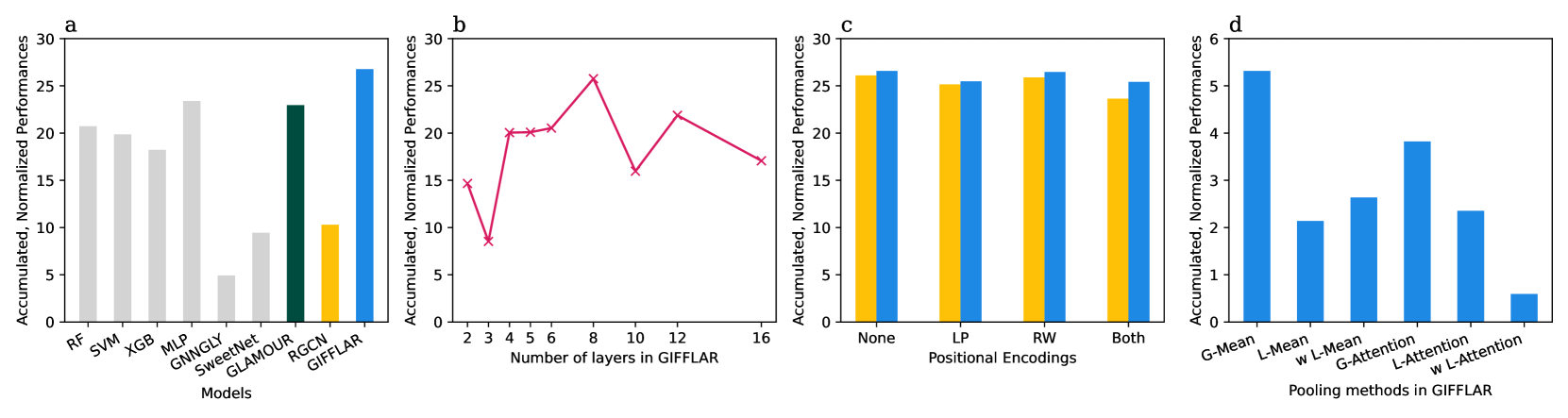
该研究在改进的GlycanML benchmark套件上进行了评估,并取得了state-of-the-art的性能。具体的性能数据和提升幅度需要在论文中查找,但摘要表明该模型显著优于现有方法,为糖链表示学习领域带来了突破。
🎯 应用场景
该研究成果可应用于计算糖科学领域,用于预测糖链的性质、功能和相互作用。这有助于深入理解糖链在生物学中的作用,例如在蛋白质修饰、细胞识别和免疫反应等方面的作用。此外,该模型还可用于药物发现,例如设计能够靶向特定糖链的药物。
📄 摘要(原文)
Glycans are the most complex biological sequence, with monosaccharides forming extended, non-linear sequences. As post-translational modifications, they modulate protein structure, function, and interactions. Due to their diversity and complexity, predictive models of glycan properties and functions are still insufficient. Graph Neural Networks (GNNs) are deep learning models designed to process and analyze graph-structured data. These architectures leverage the connectivity and relational information in graphs to learn effective representations of nodes, edges, and entire graphs. Iteratively aggregating information from neighboring nodes, GNNs capture complex patterns within graph data, making them particularly well-suited for tasks such as link prediction or graph classification across domains. This work presents a new model architecture based on combinatorial complexes and higher-order message passing to extract features from glycan structures into a latent space representation. The architecture is evaluated on an improved GlycanML benchmark suite, establishing a new state-of-the-art performance. We envision that these improvements will spur further advances in computational glycosciences and reveal the roles of glycans in biology.