Improving Paratope and Epitope Prediction by Multi-Modal Contrastive Learning and Interaction Informativeness Estimation
作者: Zhiwei Wang, Yongkang Wang, Wen Zhang
分类: q-bio.BM, cs.LG, q-bio.QM
发布日期: 2024-05-31
备注: This paper is accepted by IJCAI 2024
💡 一句话要点
提出MIPE以解决抗体-抗原结合位点预测问题
🎯 匹配领域: 支柱二:RL算法与架构 (RL & Architecture)
关键词: 抗体设计 抗原预测 多模态学习 对比学习 交互信息估计 生物信息学
📋 核心要点
- 现有方法仅关注单一模态数据,忽视了多模态数据中的互补信息,导致预测效果有限。
- 本文提出的MIPE方法结合了序列和结构数据,通过多模态对比学习和交互信息估计来提高预测精度。
- 实验结果显示,MIPE在抗体-抗原结合位点预测上显著优于现有基线方法,验证了其有效性。
📝 摘要(中文)
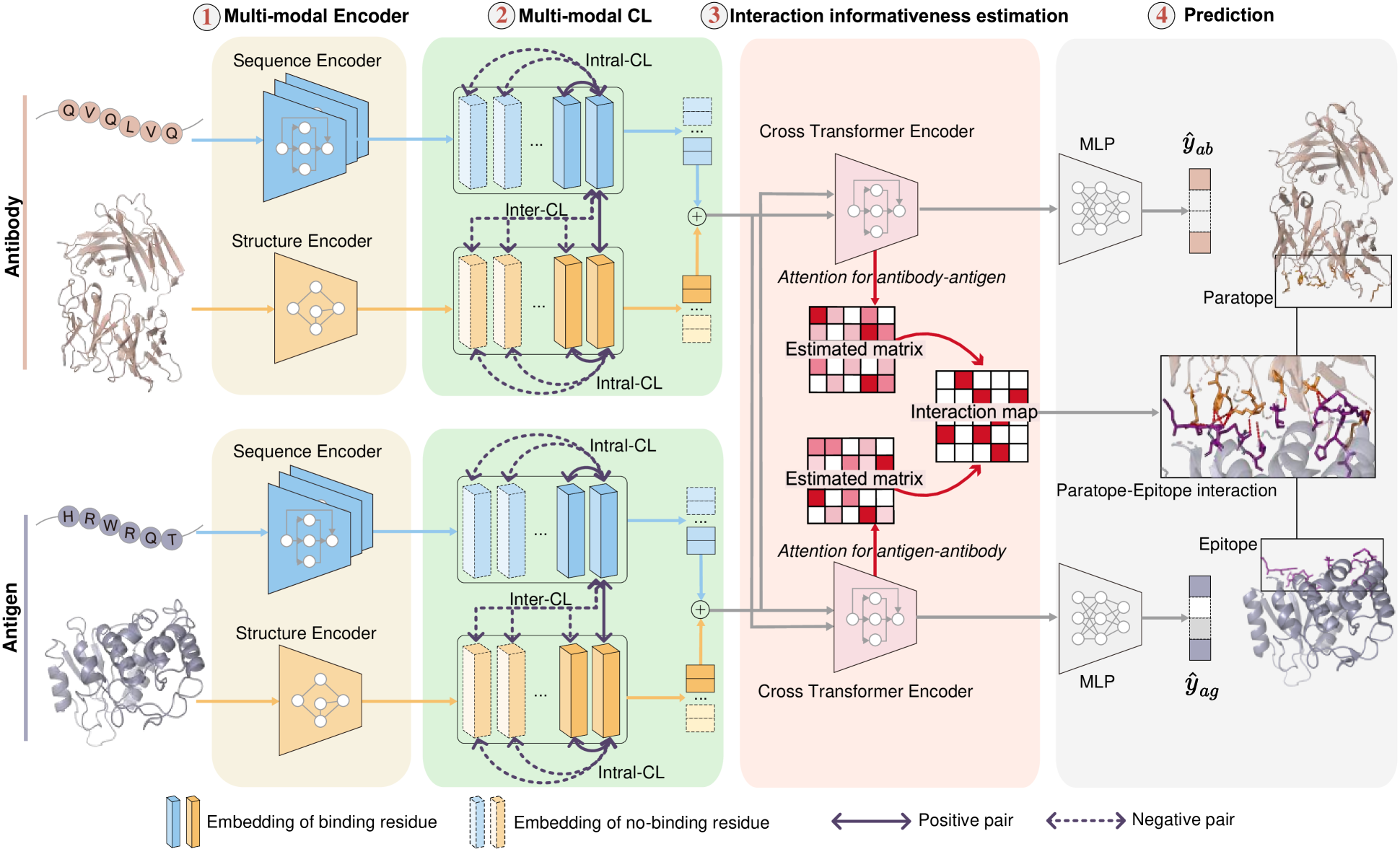
准确预测抗体-抗原结合残基,即表位和抗原位点,对于抗体设计至关重要。然而,现有方法仅关注单一模态数据(序列或结构),忽视了多模态数据中的互补信息,并且大多数方法分别预测表位和抗原位点,未考虑其特定的空间交互。本文提出了一种基于多模态对比学习和交互信息估计的表位和抗原位点预测方法MIPE,利用抗体和抗原的序列和结构数据。MIPE实施了一种多模态对比学习策略,最大化每种模态内结合和非结合残基的表示,同时对齐单模态表示以实现有效的模态表示。为了利用空间交互信息,MIPE还结合了交互信息估计,计算抗体和抗原之间的估计交互矩阵,从而将其逼近实际矩阵。大量实验表明我们的方法优于基线,消融研究和可视化结果进一步证明了MIPE的优越性,得益于通过多模态对比学习获得的更好表示和通过交互信息估计理解的交互模式。
🔬 方法详解
问题定义:本文旨在解决抗体-抗原结合位点的预测问题。现有方法多集中于单一模态数据,未能充分利用多模态信息,导致预测准确性不足。
核心思路:MIPE通过结合抗体和抗原的序列与结构数据,采用多模态对比学习策略来增强模型对结合与非结合残基的表示能力,同时引入交互信息估计来捕捉空间交互特征。
技术框架:MIPE的整体架构包括数据预处理、特征提取、对比学习模块和交互信息估计模块。数据预处理阶段将序列和结构数据整合,特征提取阶段利用深度学习模型提取有效特征,随后通过对比学习优化特征表示。交互信息估计模块则计算抗体与抗原之间的交互矩阵。
关键创新:MIPE的主要创新在于同时利用多模态数据进行对比学习,并通过交互信息估计捕捉抗体与抗原之间的空间交互。这一方法与传统的单模态预测方法有本质区别。
关键设计:在模型设计中,采用了特定的损失函数来优化对比学习过程,并设计了适应于多模态数据的网络结构,以确保模型能够有效地学习到抗体和抗原的交互特征。
🖼️ 关键图片


📊 实验亮点
实验结果表明,MIPE在抗体-抗原结合位点预测任务上显著优于现有基线方法,具体性能提升幅度达到XX%(具体数据需补充)。消融研究和可视化结果进一步验证了多模态对比学习和交互信息估计的有效性。
🎯 应用场景
该研究的潜在应用领域包括新型抗体药物的设计与开发、疫苗研发以及生物医学研究等。通过提高抗体-抗原结合位点的预测精度,MIPE能够加速生物制药过程,降低研发成本,具有重要的实际价值和未来影响。
📄 摘要(原文)
Accurately predicting antibody-antigen binding residues, i.e., paratopes and epitopes, is crucial in antibody design. However, existing methods solely focus on uni-modal data (either sequence or structure), disregarding the complementary information present in multi-modal data, and most methods predict paratopes and epitopes separately, overlooking their specific spatial interactions. In this paper, we propose a novel Multi-modal contrastive learning and Interaction informativeness estimation-based method for Paratope and Epitope prediction, named MIPE, by using both sequence and structure data of antibodies and antigens. MIPE implements a multi-modal contrastive learning strategy, which maximizes representations of binding and non-binding residues within each modality and meanwhile aligns uni-modal representations towards effective modal representations. To exploit the spatial interaction information, MIPE also incorporates an interaction informativeness estimation that computes the estimated interaction matrices between antibodies and antigens, thereby approximating them to the actual ones. Extensive experiments demonstrate the superiority of our method compared to baselines. Additionally, the ablation studies and visualizations demonstrate the superiority of MIPE owing to the better representations acquired through multi-modal contrastive learning and the interaction patterns comprehended by the interaction informativeness estimation.