CURENet: Combining Unified Representations for Efficient Chronic Disease Prediction
作者: Cong-Tinh Dao, Nguyen Minh Thao Phan, Jun-En Ding, Chenwei Wu, David Restrepo, Dongsheng Luo, Fanyi Zhao, Chun-Chieh Liao, Wen-Chih Peng, Chi-Te Wang, Pei-Fu Chen, Ling Chen, Xinglong Ju, Feng Liu, Fang-Ming Hung
分类: cs.AI
发布日期: 2025-11-14
DOI: 10.1007/s13755-025-00396-w
💡 一句话要点
CURENet:结合统一表征的高效慢性病预测多模态模型
🎯 匹配领域: 支柱二:RL算法与架构 (RL & Architecture) 支柱九:具身大模型 (Embodied Foundation Models)
关键词: 电子健康记录 多模态学习 慢性病预测 大型语言模型 Transformer 临床决策支持 时间序列分析
📋 核心要点
- 现有预测模型未能充分捕捉EHR多模态数据间的交互、冗余和时序模式,通常侧重于单一数据类型或忽略复杂性。
- CURENet通过利用LLM处理临床文本和文本型实验室测试,以及Transformer编码器处理时序就诊数据,整合EHR中的非结构化临床笔记、实验室测试和时序数据。
- 在MIMIC-III和FEMH数据集上的实验表明,CURENet在预测前10种慢性病方面取得了超过94%的准确率,验证了多模态EHR集成的潜力。
📝 摘要(中文)
本文提出了一种名为CURENet的多模态模型(结合统一表征的高效慢性病预测),旨在整合电子健康记录(EHRs)中不同类型的数据,包括非结构化的临床笔记、结构化的实验室测试和时间序列的就诊数据。CURENet利用大型语言模型(LLMs)处理临床文本和文本型实验室测试数据,并使用Transformer编码器处理纵向序列就诊数据,从而捕捉不同形式临床数据之间复杂的相互作用,并为慢性疾病创建一个更可靠的预测模型。在公共MIMIC-III和私有FEMH数据集上的评估结果表明,CURENet在多标签框架下预测前10种慢性疾病的准确率超过94%。该研究强调了多模态EHR集成在增强临床决策和改善患者预后方面的潜力。
🔬 方法详解
问题定义:论文旨在解决利用电子健康记录(EHRs)进行慢性病预测时,现有模型无法有效整合和利用多模态数据(如临床笔记、实验室测试和时序就诊数据)的问题。现有方法通常侧重于单一数据类型,忽略了不同数据模态之间的复杂交互和时序依赖关系,导致预测性能受限。
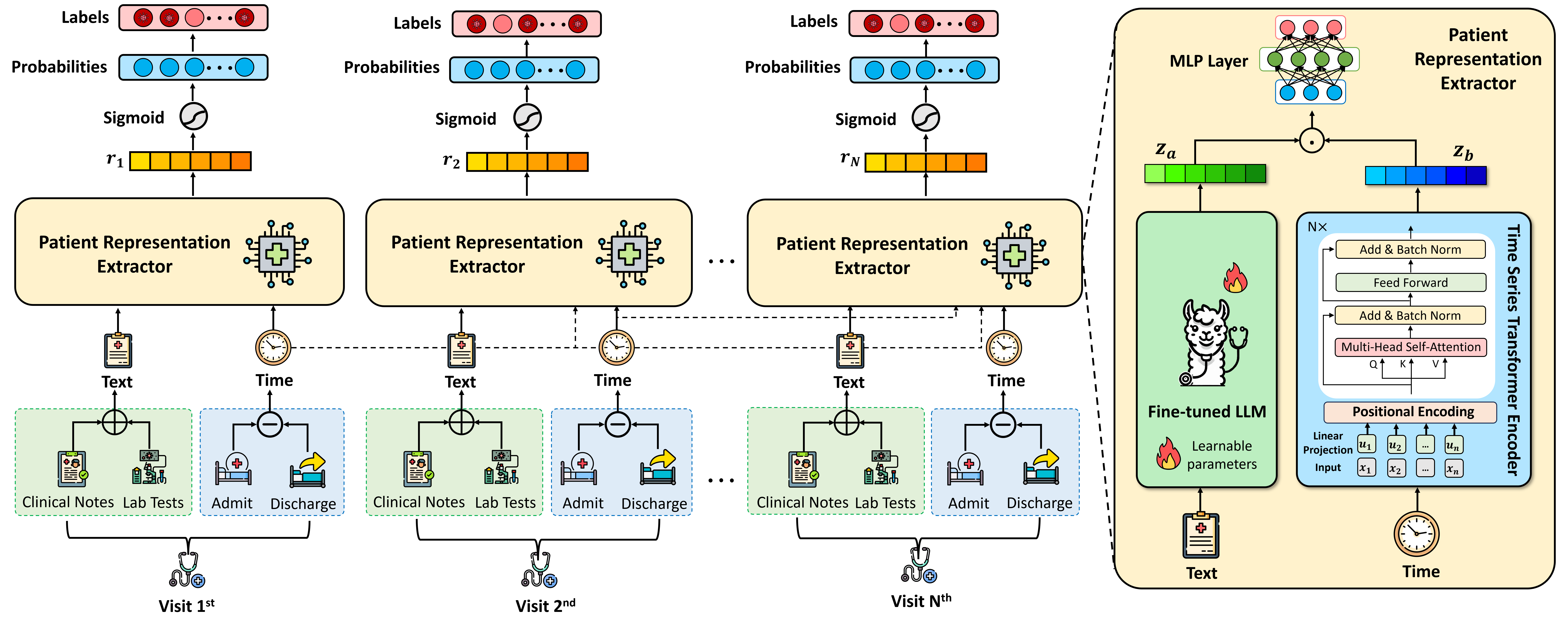
核心思路:CURENet的核心思路是利用大型语言模型(LLMs)和Transformer编码器,将不同模态的EHR数据转换为统一的表征,并学习它们之间的复杂关系。通过这种方式,模型能够更全面地理解患者的健康状况,从而提高慢性病预测的准确性。
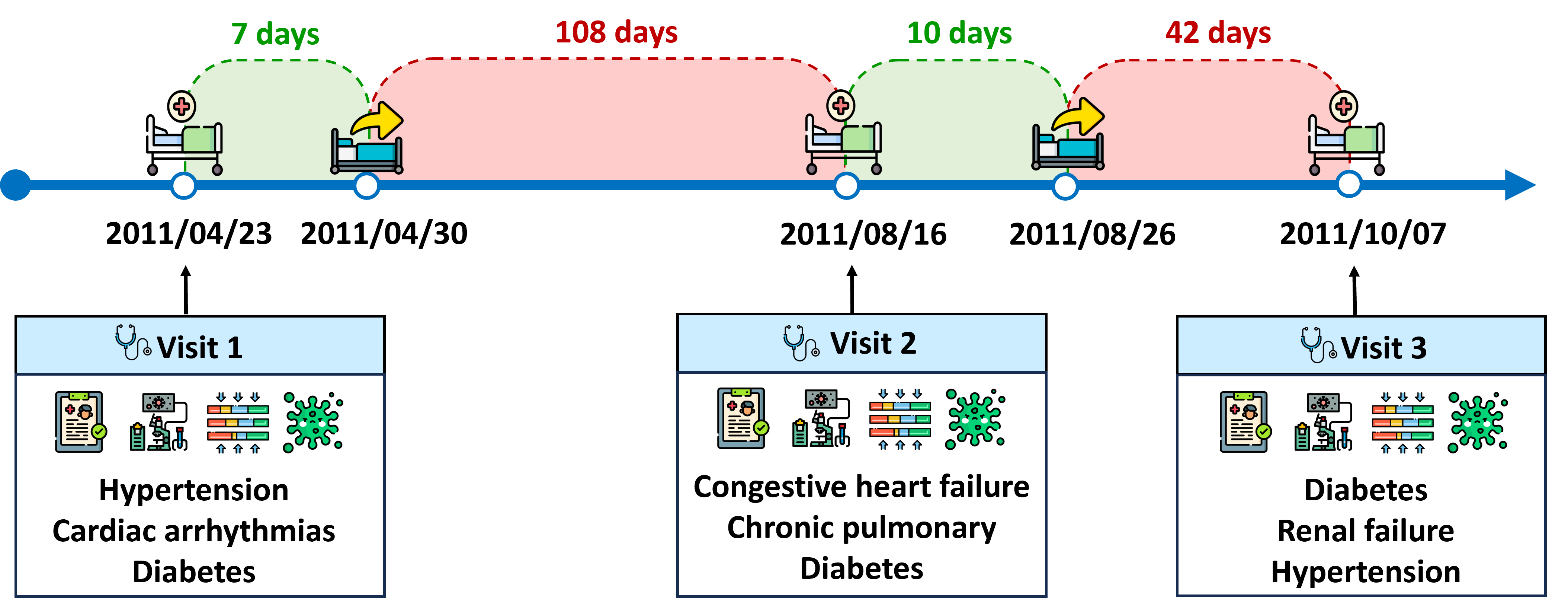
技术框架:CURENet的整体架构包含以下主要模块:1) 临床文本处理模块:使用LLM(具体模型未知)将非结构化的临床笔记转换为文本嵌入;2) 实验室测试处理模块:使用LLM将文本型实验室测试数据转换为嵌入;3) 时序就诊数据处理模块:使用Transformer编码器处理患者的时序就诊数据,捕捉时间依赖关系;4) 多模态融合模块:将来自不同模块的嵌入进行融合,形成统一的患者表征;5) 预测模块:使用融合后的表征预测患者是否患有某种慢性疾病。
关键创新:CURENet的关键创新在于其多模态融合策略,它能够有效地整合来自不同数据源的信息,并捕捉它们之间的复杂关系。与现有方法相比,CURENet能够更全面地理解患者的健康状况,从而提高慢性病预测的准确性。此外,利用LLM处理临床文本和实验室测试数据,可以有效提取关键信息,减少人工特征工程的需求。
关键设计:论文中未详细说明LLM的具体选择和训练方式,以及Transformer编码器的具体结构和参数设置。损失函数和优化器的选择也未提及。这些技术细节的缺失限制了对CURENet的深入理解和复现。
🖼️ 关键图片
📊 实验亮点
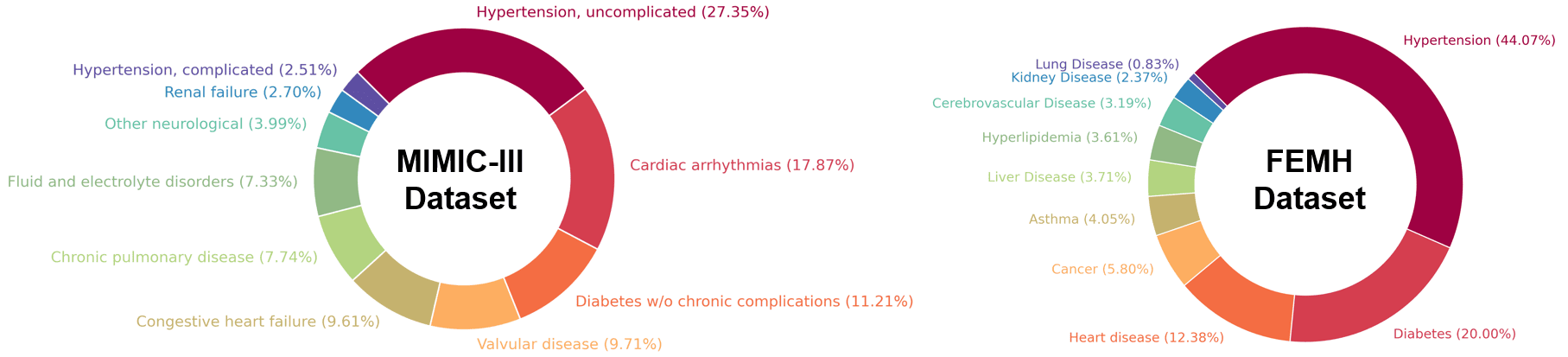
CURENet在MIMIC-III和FEMH数据集上进行了评估,结果表明其在预测前10种慢性疾病方面取得了超过94%的准确率。虽然论文中没有明确指出与哪些基线模型进行了比较,以及具体的提升幅度,但94%以上的准确率表明CURENet具有很强的竞争力,验证了多模态EHR集成在慢性病预测中的有效性。
🎯 应用场景
CURENet可应用于临床决策支持系统,帮助医生更准确地预测患者患慢性病的风险,从而制定更有效的治疗方案。该模型还可用于疾病风险评估、患者分层管理和个性化医疗等领域,具有重要的临床应用价值和社会效益。未来,该研究可扩展到其他疾病预测和健康管理任务。
📄 摘要(原文)
Electronic health records (EHRs) are designed to synthesize diverse data types, including unstructured clinical notes, structured lab tests, and time-series visit data. Physicians draw on these multimodal and temporal sources of EHR data to form a comprehensive view of a patient's health, which is crucial for informed therapeutic decision-making. Yet, most predictive models fail to fully capture the interactions, redundancies, and temporal patterns across multiple data modalities, often focusing on a single data type or overlooking these complexities. In this paper, we present CURENet, a multimodal model (Combining Unified Representations for Efficient chronic disease prediction) that integrates unstructured clinical notes, lab tests, and patients' time-series data by utilizing large language models (LLMs) for clinical text processing and textual lab tests, as well as transformer encoders for longitudinal sequential visits. CURENet has been capable of capturing the intricate interaction between different forms of clinical data and creating a more reliable predictive model for chronic illnesses. We evaluated CURENet using the public MIMIC-III and private FEMH datasets, where it achieved over 94\% accuracy in predicting the top 10 chronic conditions in a multi-label framework. Our findings highlight the potential of multimodal EHR integration to enhance clinical decision-making and improve patient outcomes.