BrainCSD: A Hierarchical Consistency-Driven MoE Foundation Model for Unified Connectome Synthesis and Multitask Brain Trait Prediction
作者: Xiongri Shen, Jiaqi Wang, Yi Zhong, Zhenxi Song, Leilei Zhao, Liling Li, Yichen Wei, Lingyan Liang, Shuqiang Wang, Baiying Lei, Demao Deng, Zhiguo Zhang
分类: q-bio.NC, cs.AI
发布日期: 2025-11-07
🔗 代码/项目: GITHUB
💡 一句话要点
提出BrainCSD以解决脑连接组合成与多任务脑特征预测问题
🎯 匹配领域: 支柱二:RL算法与架构 (RL & Architecture) 支柱九:具身大模型 (Embodied Foundation Models)
关键词: 脑连接组 多模态生物标志物 混合专家模型 功能性连接 结构性连接 脑特征预测 神经解剖学 临床应用
📋 核心要点
- 现有方法在处理脑连接组数据时面临获取成本高、预处理复杂和模态缺失等挑战,限制了其临床应用。
- 论文提出BrainCSD模型,通过层次化混合专家机制,联合合成功能性和结构性连接,支持多任务预测。
- 在多个数据集上评估,BrainCSD在MCI与CN分类中取得95.6%的准确率,且合成误差显著降低,表现优异。
📝 摘要(中文)
功能性和结构性连接(FC/SC)是脑分析的重要多模态生物标志物,但其临床应用受到获取成本高、预处理复杂和频繁缺失模态的限制。现有基础模型要么处理单一模态,要么缺乏跨模态和跨尺度一致性的明确机制。我们提出了BrainCSD,一个层次化的混合专家(MoE)基础模型,能够联合合成FC/SC生物标志物并支持下游解码任务(诊断和预测)。BrainCSD具有三个神经解剖学基础组件:特定ROI的MoE、编码-激活MoE和网络感知的精炼MoE。经过完整和缺失模态设置下的数据集评估,BrainCSD在MCI与CN分类中取得95.6%的准确率,低合成误差,以及脑龄预测和MMSE评分估计的优异表现。
🔬 方法详解
问题定义:本论文旨在解决脑连接组合成与多任务脑特征预测中的模态缺失和一致性问题。现有方法通常只能处理单一模态,缺乏有效的跨模态和跨尺度一致性机制,导致临床应用受限。
核心思路:BrainCSD模型通过层次化混合专家(MoE)结构,联合合成功能性和结构性连接,利用对比一致性和动态建模来增强不同模态之间的协同作用,从而提高预测准确性和合成质量。
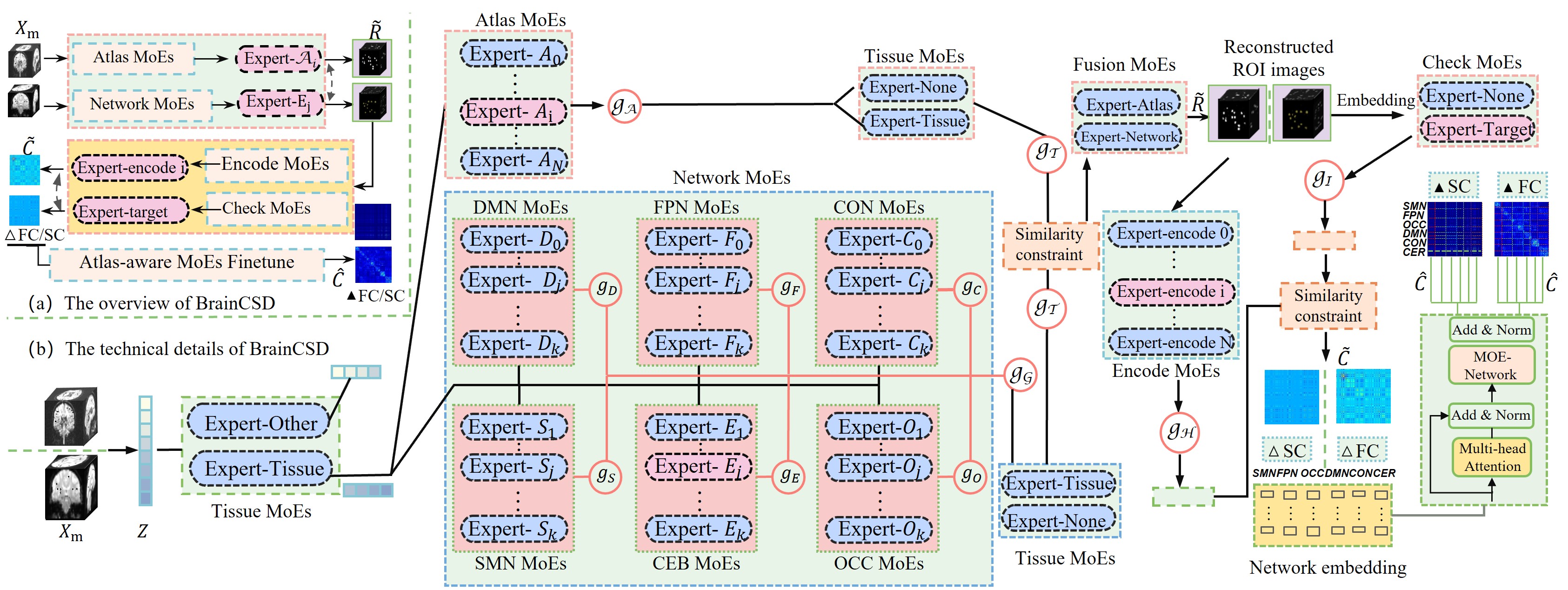
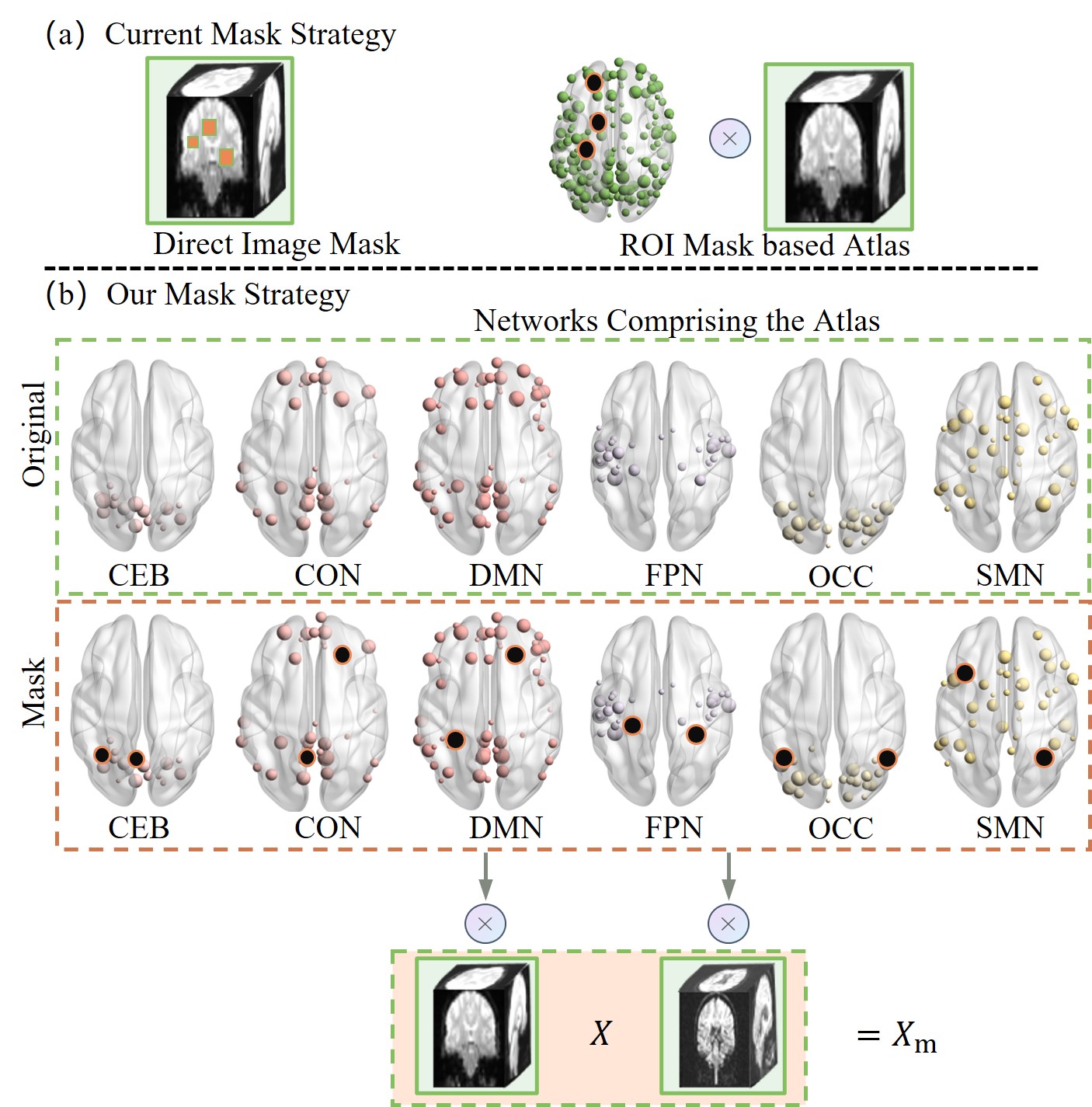
技术框架:BrainCSD的整体架构包括三个主要模块:1) ROI特定的MoE,通过对比一致性将区域激活与全局图谱对齐;2) 编码-激活MoE,建模fMRI/dMRI中的动态跨时间/梯度依赖;3) 网络感知的精炼MoE,在个体和群体层面强制结构先验和对称性。
关键创新:BrainCSD的主要创新在于其层次化的混合专家结构,能够有效处理多模态数据的合成与预测,同时引入了对比一致性机制,显著提升了模型的跨模态一致性和预测性能。
关键设计:模型设计中采用了特定的损失函数以强化对比一致性,设置了多层次的网络结构以适应不同模态的特征,确保了在缺失模态情况下的鲁棒性。
🖼️ 关键图片

📊 实验亮点
在多个数据集上,BrainCSD在MCI与CN分类中取得了95.6%的准确率,且在缺失功能性连接的情况下仍能保持较低的合成误差(FC RMSE: 0.038;SC RMSE: 0.006)。此外,模型在脑龄预测和MMSE评分估计中表现出色,MAE分别为4.04年和1.72分。
🎯 应用场景
BrainCSD模型在脑连接组分析中具有广泛的应用潜力,能够帮助临床医生更准确地进行脑疾病的诊断和预测。其在多模态数据处理上的创新设计,可能推动脑科学研究的进展,并为个性化医疗提供支持。
📄 摘要(原文)
Functional and structural connectivity (FC/SC) are key multimodal biomarkers for brain analysis, yet their clinical utility is hindered by costly acquisition, complex preprocessing, and frequent missing modalities. Existing foundation models either process single modalities or lack explicit mechanisms for cross-modal and cross-scale consistency. We propose BrainCSD, a hierarchical mixture-of-experts (MoE) foundation model that jointly synthesizes FC/SC biomarkers and supports downstream decoding tasks (diagnosis and prediction). BrainCSD features three neuroanatomically grounded components: (1) a ROI-specific MoE that aligns regional activations from canonical networks (e.g., DMN, FPN) with a global atlas via contrastive consistency; (2) a Encoding-Activation MOE that models dynamic cross-time/gradient dependencies in fMRI/dMRI; and (3) a network-aware refinement MoE that enforces structural priors and symmetry at individual and population levels. Evaluated on the datasets under complete and missing-modality settings, BrainCSD achieves SOTA results: 95.6\% accuracy for MCI vs. CN classification without FC, low synthesis error (FC RMSE: 0.038; SC RMSE: 0.006), brain age prediction (MAE: 4.04 years), and MMSE score estimation (MAE: 1.72 points). Code is available in \href{https://github.com/SXR3015/BrainCSD}{BrainCSD}