Musculoskeletal simulation of limb movement biomechanics in Drosophila melanogaster
作者: Pembe Gizem Özdil, Chuanfang Ning, Jasper S. Phelps, Sibo Wang-Chen, Guy Elisha, Alexander Blanke, Auke Ijspeert, Pavan Ramdya
分类: q-bio.NC, cs.AI, cs.LG, cs.RO
发布日期: 2025-09-08 (更新: 2025-09-11)
备注: 23 pages, 11 figures
💡 一句话要点
构建果蝇腿部肌肉骨骼模型,揭示运动控制的生物力学机制
🎯 匹配领域: 支柱一:机器人控制 (Robot Control) 支柱二:RL算法与架构 (RL & Architecture)
关键词: 肌肉骨骼模型 果蝇 生物力学 运动控制 OpenSim MuJoCo 模仿学习
📋 核心要点
- 现有果蝇神经系统、肌肉和外骨骼的重建数据丰富,但缺乏解剖学和物理学上合理的腿部肌肉模型,无法连接神经活动和关节运动。
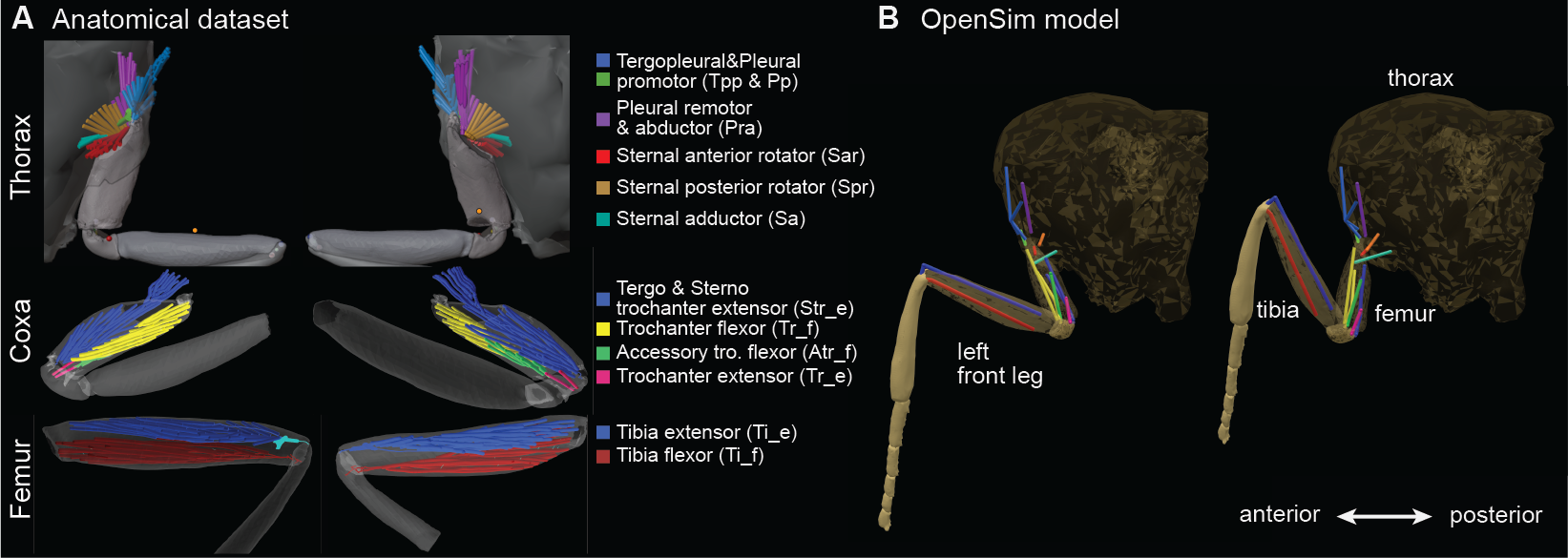
- 论文构建了首个基于数据的果蝇腿部3D肌肉骨骼模型,使用Hill型肌肉表示,并结合形态学成像数据优化肌肉参数。
- 通过肌肉驱动的行为重现和模仿学习,验证了模型的有效性,并揭示了被动关节属性对运动学习的影响。
📝 摘要(中文)
本文提出了一种基于数据的果蝇腿部3D肌肉骨骼模型,该模型在OpenSim和MuJoCo模拟环境中实现。该模型结合了基于多个固定样本高分辨率X射线扫描的Hill型肌肉表示。论文提出了一套利用形态学成像数据构建肌肉模型并优化果蝇特有未知肌肉参数的流程。通过结合肌肉骨骼模型和行为果蝇的详细3D姿态估计数据,实现了OpenSim中的肌肉驱动行为重现。对不同行走和梳理行为的肌肉活动模拟预测了可实验验证的协同肌肉活动。此外,通过在MuJoCo中训练模仿学习策略,测试了不同被动关节属性对学习速度的影响,发现阻尼和刚度有助于学习。该模型有助于研究实验可控模型生物中的运动控制,深入了解生物力学对复杂肢体运动产生的贡献。此外,该模型可用于控制具身人工智能体,在模拟环境中生成自然且柔顺的运动。
🔬 方法详解
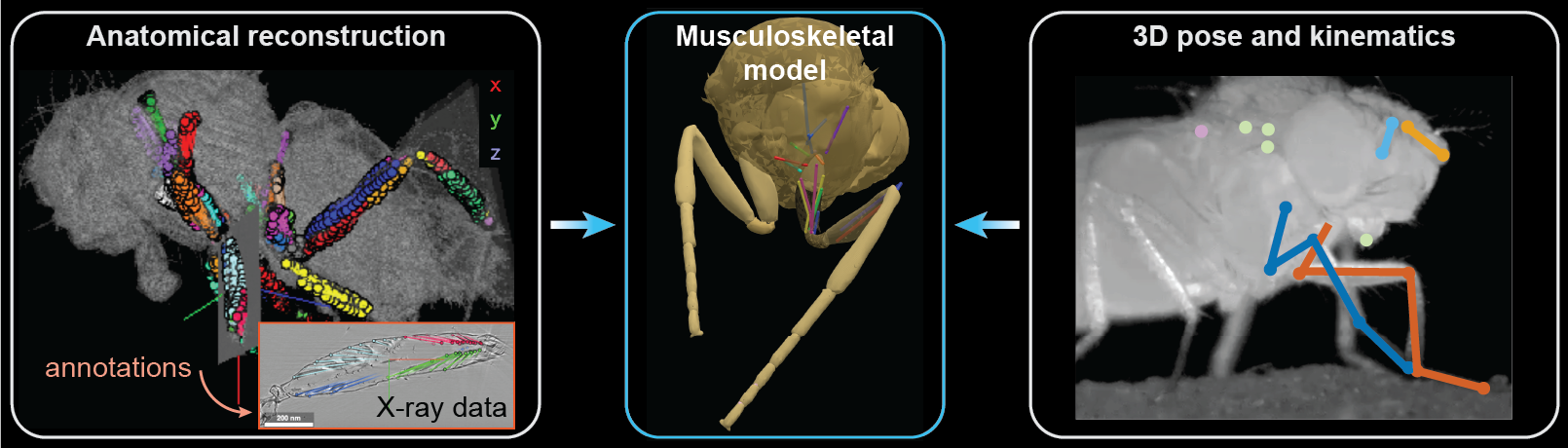
问题定义:论文旨在解决缺乏果蝇腿部肌肉骨骼模型的问题。现有方法无法将神经活动与关节运动联系起来,阻碍了对果蝇运动控制机制的深入理解。缺乏这种模型也限制了对生物力学在复杂肢体运动产生中的作用的探究。
核心思路:论文的核心思路是构建一个基于数据的3D肌肉骨骼模型,该模型能够准确地表示果蝇腿部的肌肉和骨骼结构,并能够模拟肌肉活动对关节运动的影响。通过结合高分辨率的形态学数据和行为数据,可以优化模型的参数,使其能够准确地预测果蝇的运动行为。
技术框架:该研究的技术框架主要包括以下几个步骤:1) 使用高分辨率X射线扫描获取果蝇腿部的形态学数据;2) 基于形态学数据构建3D肌肉骨骼模型,包括骨骼、关节和肌肉;3) 使用Hill型肌肉模型表示肌肉的力学特性;4) 使用行为数据优化肌肉模型的参数;5) 在OpenSim和MuJoCo模拟环境中进行肌肉驱动的行为重现和模仿学习。
关键创新:该论文的关键创新在于构建了首个基于数据的果蝇腿部3D肌肉骨骼模型。该模型结合了高分辨率的形态学数据和行为数据,能够准确地表示果蝇腿部的肌肉和骨骼结构,并能够模拟肌肉活动对关节运动的影响。此外,该论文还提出了一套利用形态学成像数据构建肌肉模型并优化果蝇特有未知肌肉参数的流程。
关键设计:在肌肉建模方面,使用了Hill型肌肉模型,该模型能够较好地描述肌肉的力学特性。在参数优化方面,使用了行为数据作为优化目标,使得模型能够更好地预测果蝇的运动行为。在模仿学习方面,探索了不同被动关节属性(如阻尼和刚度)对学习速度的影响。
🖼️ 关键图片

📊 实验亮点
论文通过肌肉驱动的行为重现,验证了模型的有效性,并预测了可实验验证的协同肌肉活动。此外,通过在MuJoCo中训练模仿学习策略,发现阻尼和刚度等被动关节属性能够显著提高学习速度。这些结果表明,该模型能够准确地模拟果蝇的运动行为,并为研究运动控制的生物力学机制提供了有力的工具。
🎯 应用场景
该研究成果可应用于生物力学、神经科学和机器人学等领域。在生物力学和神经科学领域,该模型可以帮助研究人员深入理解果蝇的运动控制机制,揭示生物力学在复杂肢体运动产生中的作用。在机器人学领域,该模型可以用于控制具身人工智能体,在模拟环境中生成自然且柔顺的运动,从而提高机器人的运动能力和适应性。
📄 摘要(原文)
Computational models are critical to advance our understanding of how neural, biomechanical, and physical systems interact to orchestrate animal behaviors. Despite the availability of near-complete reconstructions of the Drosophila melanogaster central nervous system, musculature, and exoskeleton, anatomically and physically grounded models of fly leg muscles are still missing. These models provide an indispensable bridge between motor neuron activity and joint movements. Here, we introduce the first 3D, data-driven musculoskeletal model of Drosophila legs, implemented in both OpenSim and MuJoCo simulation environments. Our model incorporates a Hill-type muscle representation based on high-resolution X-ray scans from multiple fixed specimens. We present a pipeline for constructing muscle models using morphological imaging data and for optimizing unknown muscle parameters specific to the fly. We then combine our musculoskeletal models with detailed 3D pose estimation data from behaving flies to achieve muscle-actuated behavioral replay in OpenSim. Simulations of muscle activity across diverse walking and grooming behaviors predict coordinated muscle synergies that can be tested experimentally. Furthermore, by training imitation learning policies in MuJoCo, we test the effect of different passive joint properties on learning speed and find that damping and stiffness facilitate learning. Overall, our model enables the investigation of motor control in an experimentally tractable model organism, providing insights into how biomechanics contribute to generation of complex limb movements. Moreover, our model can be used to control embodied artificial agents to generate naturalistic and compliant locomotion in simulated environments.